به گزارش سرویس فناوری اطلاعات«خبرنامه دانشجویان ایران»؛ بیوانفورماتیک، به عنوان یک رشته جدید در حال ظهور، ریاضیات، فناوری اطلاعات و زیست شناسی را ترکیب کرده و به پاسخگویی به سوالات بیولوژیکی کمک میکند. کلمه «بیوانفورماتیک» برای اولین بار در سال 1968 استفاده شد و تعریف آن برای اولین بار در سال 1978 ارائه شد. بیوانفورماتیک همچنین به عنوان زیست شناسی محاسباتی نامیده شده است.

اجزای اصلی بیوانفورماتیک عبارتند از توسعه ابزارها و الگوریتمهای نرم افزاری و تجزیه و تحلیل و تفسیر دادههای بیولوژیکی با استفاده از انواع ابزارهای نرم افزاری و الگوریتمهای خاص.بیوانفورماتیک به عنوان شاخهای بین رشتهای از علوم زیستی، توسعه روشهای شناختی، تجزیه و تحلیل برای کشف مقادیر وسیع پایگاه دادههای بیولوژیکی جهت پشتیبانی از ذخیره سازی، ترتیب، سیستم بندی، درک و اجرای دادههای بیولوژیکی و به عنوان یک وسیله مورد آزمایش برای تحقیقات ژنوم و محصول ژنتیکی استفاده میشود. این ابزارها شامل انفورماتیک سنتی، مدرن و محاسبات ابری، آمار و ریاضیات و تشخیص الگو، بازسازی، یادگیری ماشینی، شبیه سازی، مدل سازی مولکولی و الگوریتمهای مربوط به فولدینگ ساختارها است. با این حال، رشد و پیشرفت حوزه دانش بیولوژیکی ارتباط تنگاتنگی با نرم افزار و برنامه نویسی کامپیوتری دارد و برای مدیریت مقادیر زیادی از توالیهای مولکولی DNA ، RNA، پروتئینها، متابولیتها و تجزیه و تحلیل ساختاری و عملکردی مورد نیاز است.
نرم افزارهای بیوانفورماتیک در زمینههای مختلف علوم مورد استفاده قرار میگیرند،ابزارهای کامپیوتری هستند که دقت و سرعت اجرای فعالیتهای آزمایشگاهی و پروژههای تحقیقاتی را افزایش میدهند. در این گزارش ، با مهمترین نرم افزارهای بیوانفورماتیک مورد استفاده در این رشته آشنا می شوید.
Vector NTI (1
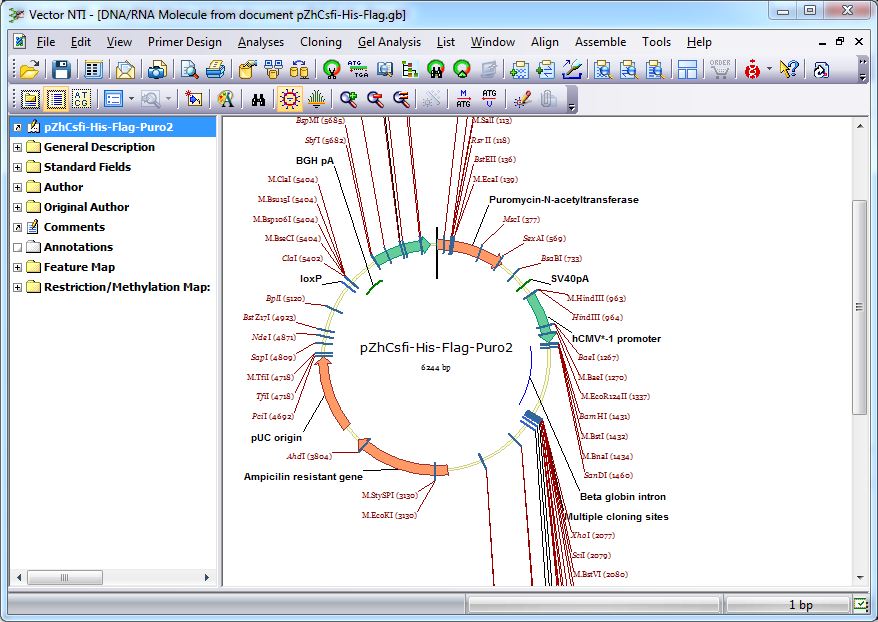
نرم افزار Invitrogen Vector NTI مجموعهای کاملاً یکپارچه از ابزارهای تجزیه و تحلیل و طراحی توالی است. این نرم افزار از شما در مدیریت، نمایش، تجزیه و تحلیل، تبدیل، به اشتراک گذاری و انتشار انواع مختلف دادههای بیولوژیکی مولکولی در یک محیط تجزیه و تحلیل با کیفیت بالا پشتیبانی میکند. به عنوان مثال، به محققان اجازه میدهد تا قبل از انجام آزمایش در آزمایشگاه، آزمایش شبیه سازی DNA را بر روی کامپیوتر برنامه ریزی کنند.
این برنامه دارای امکاناتی است که در ادامه آن ها را می بینید.
• ایجاد، حاشیه نویسی، تجزیه و تحلیل و به اشتراک گذاری توالی DNA یا پروتئین
• انجام و ذخیره جستجوهای BLAST
• طراحی پرایمرها برای PCR، شبیه سازی، تعیین توالی یا آزمایش هیبریداسیون
• برنامه ریزی انجام کلونینگ و ران کردن ژل در محیط In – Silico
• ترازبندی توالی چند پروتئین یا DNA
• جستجو در NCRE’s Entrez و مشاهده و ذخیره پروتئینها
• ویرایش دادههای کروماتوگرام، جمع آوری آنها
با استفاده از ابزار Vector NTI data export میتوانید دادههای مولکولی خود را از قالبهای فایل Vector NTI دارای حق چاپ به فرمتهای استاندارد منبع باز صادر کنید. نرم افزار Vector NTI Express Designer یک راه حل پیشگامانه برای اجرای فنی شبیه سازی و مونتاژ In – Silico نسل بعدی است. رابط کاربری که به تازگی توسعه یافته است، یک جدول ساخت مجازی را برای ساختارهای وکتور کشیدن و رها کردن ساده و مقایسه توالی ساده بین پروژهها ارائه میدهد. نرم افزار Vector NTI Express Designer همچنین دسترسی به ابزارهای وب Invitrogen GeneArt برای دستیابی به سطوح بهینه بیان پروتئین را تسهیل میکند. نرم افزار بیوانفورماتیک Vector NTI Express Designer اکنون برای سیستم عاملهای Mac یا PC در دسترس است.
GALAXY (2
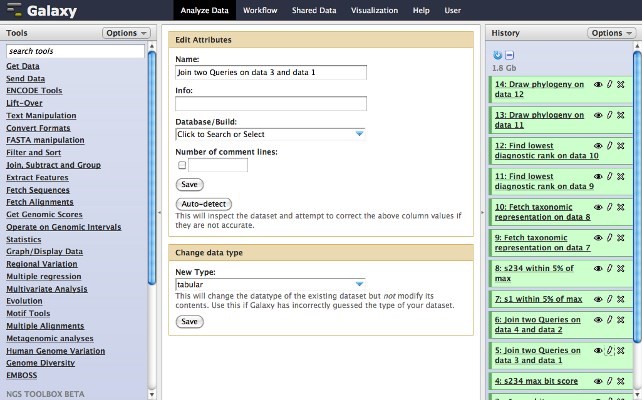
Galaxy یک پلت فرم باز و مبتنی بر وب در دسترس و یکی از نرم افزارهای بیوانفورماتیک قابل تولید و شفاف برای تحقیقات محاسباتی است. GALAXY یک نرمافزار محبوب است که به طور گستردهای در یکپارچه سازی دادهها، آنالیز و ماندگاری دادهها برای زیست شناسی محاسباتی در کنار یک سستم عامل مانند UNIX در دسترس افراد است.
این ابزار بیوانفورماتیک دارای مزایای زیادی است که در ادامه آن ها را می بینید.
• قابل دسترس بودن: تجربه برنامه نویسی برای بارگذاری آسان دادهها، اجرای ابزارهای پیچیده و گردش کار و تجسم نتایج، در استفاده از این نرم افزار مورد نیاز نیست.
• قابل تکرار بودن: GALAXY اطلاعات را ضبط میکند تا کاربر مجبور نباشد هر دفعه آنها را ذخیره کند. هر کاربری میتواند یک تحلیل محاسباتی کامل از پارامترهای ابزاری گرفته تا «درخت وابستگی» (dependency tree) را تکرار و درک کند.
• شفاف سازی: کاربران این پلتفرم سابقه، گردش کار و تجسمات خود را از طریق وب به اشتراک میگذارند و منتشر میکنند.
• جامعه محور بودن: کاربران فراگیر و متنوع (توسعه دهندگان، مربیان، محققان، پزشکان و غیره) دارای اختیار هستند که یافتههای خود را به اشتراک بگذارند.
کاربردهای GALAXY شامل مطالعه در بیان ژن، پروتئومیکس، ترنسکریپتومیکس، «آنالیز توالی یابی نسل بعدی» (NGS) و مونتاژ ژنوم است.
Chromas (3
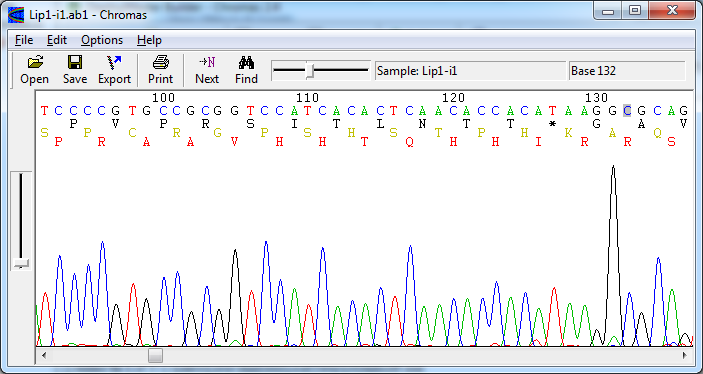
Chromas یک نمایشگر و ویرایشگر رایگان، ساده و کاربر – پسند برای استفاده جهت کروماتوگرامهای حاصل از توالییابی سنگر است. این برنامه دارای گزینههای تبدیل فرمت بسیاری از جمله توابع پردازش دستهای برای مدیریت همزمان بسیاری از فایلها است. Chromas دارای ویژگیهای بسیاری است از جمله اینکه انواع فایلهای کروماتوگرام با فرمت SCF و ZTR را باز میکند که توسط ترتیب دهندههای دیگر ایجاد شده یا از پایگاه دادهها بازیابی شده اند.
قابلیت چاپ کروماتوگرام را با گزینههای بزرگنمایی یا متناسب با یک صفحه میدهد. توالیهای با کیفیت پایین یا توالی وکتورها را در صورت موجود بودن دادههای با کیفیت حذف میکند.توالیها را در متن ساده مانند FASTA ، FASTQ ، EMBL ، GenBank یا فرمتهای GCG خروجی میدهد یا به صورت بازهای شمارهگذاری شده آنها را ارائه میدهد. توالی را در کلیپ بورد با متن ساده، قالب FASTA یا FASTQ برای چسباندن به سایر برنامهها کپی میکند. توالی و کروماتوگرام را برعکس و مکمل میکند، زیر توالیها را با مطابقت دقیق یا ترازبندی بهینه جستجو میکند. ترجمهها را در 3 فریم همراه با توالی نمایش میدهد، میتوانید به کمک آن یک تصویر از بخش کروماتوگرام را برای چسباندن در اسناد یا ارائهها کپی کنید. ChromasPro برای مونتاژ توالی خوانده شده در کانتیگها، همراه با ویرایشگر پیکربندی گرافیکی است که کروماتوگرامهای تراز را نمایش می دهد.
AutoDimer (4
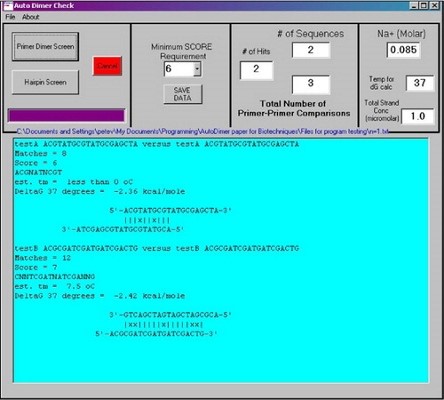
AutoDimer یکی از نرم افزارهای بیوانفورماتیک است که برای غربالگری سریع پرایمرهای PCR قبلاً انتخاب شده برای تعامل ساختارهای پرایمر – دایمر و سنجاق – سری در الیگومرهای DNA کوتاه (کمتر از 30 نوکلئوتید) توسعه داده شده است. AutoDimer در ابتدا برای کمک به توسعه روشهای «PCR چندگانه» (Multiplex – PCR) برای بررسی نشانگرهای STR و SNP برای اهداف پزشکی قانونی ایجاد شد.
Oligo(5
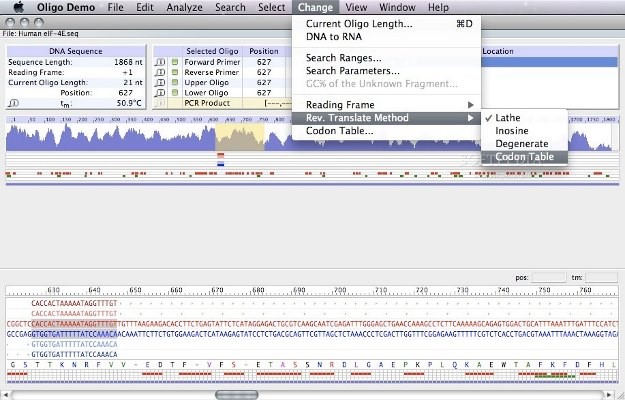
OLIGO یکی از نرم افزارهای بیوانفورماتیک تجزیه و تحلیل پرایمر و یک ابزار ضروری برای طراحی و تجزیه و تحلیل توالی و پرایمرهای PCR، ژنهای مصنوعی و انواع پروبها از جمله siRNA و تنظیم کنندههای مولکولی است. بر اساس به روزترین دادههای ترمودینامیکی نزدیکترین همسایه، الگوریتمهای جستجوی Oligo پرایمرهای بهینهای برای PCR، از جمله TaqMan ، پرایمرهای چندگانه، اجماعی یا انحطاط یافته، پیدا میکنند. پردازش دستهای فایلهای متعدد توسط این نرم افزار بیوانفورماتیک امکان پذیر است. همچنین یک ابزار ارزشمند برای «جهش زایی به کار رفته در محل» (site directed mutagenesis) است.
برای هر تک پرایمر یا جفت پرایمر، پنجرههای مختلف تجزیه و تحلیل Oligo تعداد زیادی اطلاعات مفید مانند ساختار ثانویه DNA و RNA، تشکیل دایمر، پرایمینگ غلط و همولوژی، ثبات داخلی، ترکیب و خواص فیزیکی را نشان میدهد. با استفاده از Oligo میتوانید فریمهای باز خواندن را تا وزن مولکولی پیش بینی شده و pKa پروتئینها تجزیه و تحلیل کرده و محلهای آنزیم محدود کننده را نه تنها در DNA بلکه در پروتئینهای معکوس نیز جستجو کنید. اولین نسخه نرم افزار در سال 1989 در بازار ظاهر شد. این برنامه چندین تغییر را انجام داد و آخرین مورد، تغییر از نسخه 6 به 7، جامع ترین آن بود. Oligo 7 میتواند بطور خودکار پرایمرهای چندگانه را انتخاب کرده، فایلهای توالی را در حالتهای دستهای پردازش کند، بطور خودکار پرایمرهای PCR را طراحی میکند تا چندین ناحیه DNA را در یک جستجو بپوشاند و به طور خودکار مجموعه پرایمر/پروب را برای Real – time PCR پیدا میکند یا مجموعه پرایمرهای تو در تو را پیدا میکند.
پروتکلهای جستجوی Oligo (سیستم امتیاز دهی) ممکن است به طور جزئی سفارشی شوند، بنابراین میتوانید نتایج را با توجه به نیازهای خاص خود بهینه کنید. Oligo بر روی مکینتاش و ویندوز اجرا میشود. عملکرد جامع OLIGO با چندین برنامه طراحی اولیه پرایمر تجاری کنار هم مطابقت دارد، بنابراین میتوانید پروبهایی را برای تجزیه و تحلیل توان بالا طراحی کنید، آنها را چندتایی کنید یا بر روی مجموعهای از پرایمر/پروبها تمرکز کنید و آن را برای یک برنامه جدید که هنوز منتشر نشده است بهینه کنید.
Chimera(6
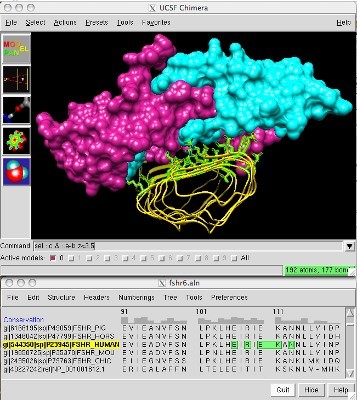
UCSF Chimera یک برنامه برای تجسم و تحلیل تعاملی ساختارهای مولکولی و دادههای مربوطه، از جمله نقشههای چگالی، مسیرها و ترازهای توالی است. کایمرا یکی از نرم افزارهای بیوانفورماتیک است که برای استفاده غیر تجاری به صورت رایگان در دسترس است. ChimeraX نسبت به Chimera عملکرد بسیار بهتر برای کار با ساختارهای بزرگ و سایر مزایای عمده و ویژگیهای کاملاً جدیدی دارد. با استفاده از این نرم افزار میتوانید تصاویر و فیلمهای با کیفیت بالا ایجاد کنید. Chimera شامل مستندات کامل است و میتوان آن را به صورت رایگان برای استفاده غیر تجاری بارگیری کرد. Chimera توسط RBVI یا منبع برای محاسبات زیستی، تجسم و انفورماتیک در دانشگاه کالیفرنیا، سان فرانسیسکو توسعه یافته است.
برخی از مهمترین ویژگیهای این نرم افزار در ادامه بیان شده اند.
• شناسایی خودکار اتم
• افزودن هیدروژن و تعیین بار جزئی
• اندازه گیری فواصل، زوایا، مساحت سطح و حجم
• ایجاد آسان ویژگیهای سفارشی با ورودیهای ساده فایل متنی
• بسیاری از فرمتها خوانده میشوند، PDB و Mol2 نوشته میشوند.
• گرفتن تصاویر با وضوح بالا
• جلوههای بصری شامل اعلان عمق، سایههای تعاملی، لبههای محیط مرئی، پسزمینههای چند رنگ
• نمایش مولکولی استاندارد
• برچسب گذاری با متن، نمادها، فلشها، کلیدهای رنگی
• ساختارهای مختلف را میتوان متفاوت و در هر زاویه برش داد
• رابط گرافیکی ساده برای ایجاد تعاملی فیلم
• تنظیم آستانه تعاملی، سطوح چندگانه (مش یا جامد)، رندرهای شفاف
• مطابقت مختصات اتمی با نقشهها و نقشهها با هم
• دارا بودن ابزارهای زیادی برای تقسیم بندی و ویرایش نقشهها
• قابلیت خواندن، نوشتن و ویرایش بسیاری از قالبهای هم ترازی توالی
• امکان جستجو BLAST پروتئین از طریق سرویس وب
SnapGene (7
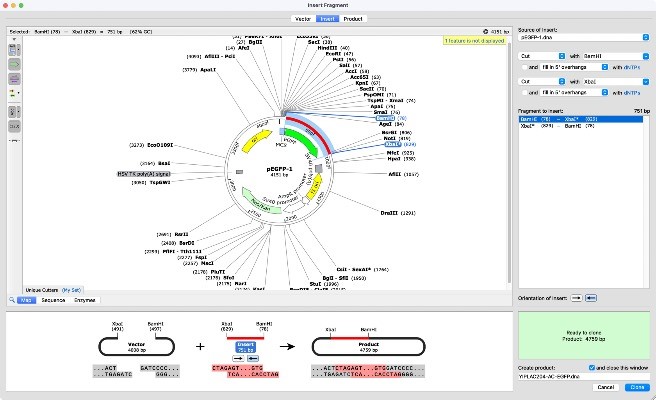
SnapGene یکی از نرم افزارهای بیوانفورماتیکی و روشی آسان و مطمئن را برای برنامه ریزی، تجسم و مستند سازی روشهای زیست شناسی مولکولی روزمره امکان پذیر میکند. این نرم افزار با رابط بصری، تجسم توالی DNA، حاشیه نویسی توالی، ویرایش توالی، شبیه سازی و تجسم پروتئین روشهای رایج شبیه سازی را امکان پذیر میکند. این نرم افزار همچنین مستندسازی و به اشتراک گذاری دادهها را امکان پذیر میکند.
ویژگیهای کلیدی این نرم افزار بیوانفورماتیکی شامل موارد زیر هستند:
• SnapGene تجسم و شبیه سازی دستکاریهای DNA شما را آسان میکند و خطاها را قبل از وقوع به شما هشدار میدهد.
• هرگونه دستکاری DNA در SnapGene به طور خودکار ثبت میشود، بنابراین میتوانید دقیقاً آنچه را انجام داده اید ببینید و توالیهای سازههای اجدادی را بازیابی کنید.
• فایلهای nna SnapGene را میتوان توسط SnapGene Viewer رایگان بین پلتفرمها باز کرد و به شما امکان میدهد نقشهها و توالیهای حاشیه نویسی شده فراوانی را با همکاران به اشتراک بگذارید.
• SnapGene به طور خودکار یک رکورد از هر روش ویرایش و شبیه سازی دنباله ایجاد میکند، بنابراین شما حتی پس از خروج یکی از اعضای آزمایشگاه، نحوه ساخت یک سازه را از دست نخواهید داد.
• SnapGene از تعداد زیادی فرمت فایل پشتیبانی میکند در نتیجه، دانشمندان میتوانند بدون از دست دادن دادهها به طور کامل به SnapGene روی آورند یا میتوانند بدون درگیری به استفاده از نرم افزار قدیمی همراه با SnapGene ادامه دهند.
BLAST (8
بلاست یا Basic Local Alignment Search Tool در دسته ابزارهای همسان سازی و بررسی شباهت قرار میگیرد. این ابزار مجموعهای از برنامههای جستجو است که برای پلتفرم Windows طراحی شده است و از آن برای جستجوهای شباهت سریع بدون توجه به اینکه پروتکل برای پروتئین است یا DNA میتوانید انجام دهید. مقایسه توالیهای نوکلئوتیدی در پایگاه داده را نیز میتوان با استفاده از این ابزار انجام داد. همچنین میتوان از طریق این ابزار آنلاین یک پایگاه داده پروتئین را برای یافتن مطابقت با توالی پروتئین مورد نظر جستجو کرد. NCBI همچنین سیستم نوبت دهی جدید را به نام Q BLAST به بلاست اضافه کرده است که به کاربران امکان میدهد نتایج را به دلخواه خود بازیابی کرده و نتایج خود را چندین بار با گزینههای قالببندی مختلف اجرا کنند.
بسته به نوع توالیهای مورد مقایسه، برنامههای مختلفی در BLAST وجود دارد که شامل موارد زیر هستند:
• blastp توالی پرس و جو آمینو اسید را با پایگاه داده توالی پروتئین مقایسه میکند.
• blastn توالی پرس و جو نوکلئوتیدی را با پایگاه داده توالی نوکلئوتیدی مقایسه میکند.
• blastx یک توالی پرس و جو نوکلئوتیدی ترجمه شده در تمام فریمهای خواندن را با پایگاه داده توالی پروتئین مقایسه میکند.
MEGA (9

نرم افزار تجزیه و تحلیل ژنتیک تکاملی مولکولی (MEGA)، که در حال حاضر دارای امکاناتی برای ایجاد ترازهای توالی، استنباط تاریخ فیلوژنتیک و انجام تجزیه و تحلیل تکاملی مولکولی است. در نسخه 6 MEGA اکنون استنتاج درختان زمانی را امکان پذیر میکند، زیرا روش RelTime را برای برآورد زمان واگرایی برای همه نقاط انشعاب در فیلوژنی پیاده سازی میکند. یک امکان جدید Timetree در MEGA6 با ارائه یک رابط کاربری گرافیکی (GUI) برای مشخص کردن قدم به قدم محدودیتهای فیلوژنی و کالیبراسیون، این استنباط درخت را تسهیل میکند. این نسخه همچنین شامل الگوریتمهای پیشرفتهای برای جستجوی درختان مطلوب تحت معیارهای تکاملی است و مدیریت حافظه پیشرفتهتری را پیاده سازی میکند که میتواند اندازه مجموعه دادههای توالی را که MEGA برای آنها قابل استفاده است، دو برابر کند. هر دو نسخه GUI و نسخه قابل فرمان دادن MEGA6 را میتوانید از www.megasoftware.net به صورت رایگان دانلود کنید.
Mauve(10
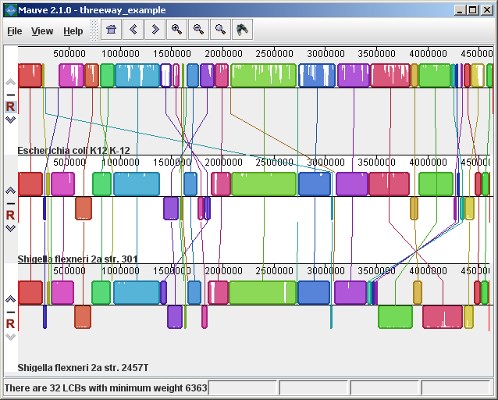
Mauve یک سیستم برای ایجاد ترازبندی کارآمد چند ژنومی در حضور رویدادهای تکاملی در مقیاس بزرگ مانند بازآرایی و وارونگی است. هم ترازی چندگانه ژنوم، زمینهای برای تحقیقات در زمینه ژنومیک مقایسهای و مطالعه پویایی تکاملی فراهم میکند. تراز کردن ژنومهای کل یک مسئله اساساً متفاوت از تراز کردن توالیهای کوتاه است. Mauve با این ایده توسعه یافته است که یک همسو کننده ژنوم چندگانه فقط به منابع محاسباتی متوسط نیاز دارد. این روش از تکنیکهای الگوریتمی استفاده میکند که از نظر میزان توالی هم تراز به خوبی مقیاس میشوند. به عنوان مثال، یک جفت ژنوم Y. pestis را میتوان در کمتر از یک دقیقه تراز کرد، در حالی که یک گروه 9 ژنومی واگرا انتروباکتریال را میتوان در چند ساعت تراز کرد.
VMD (11
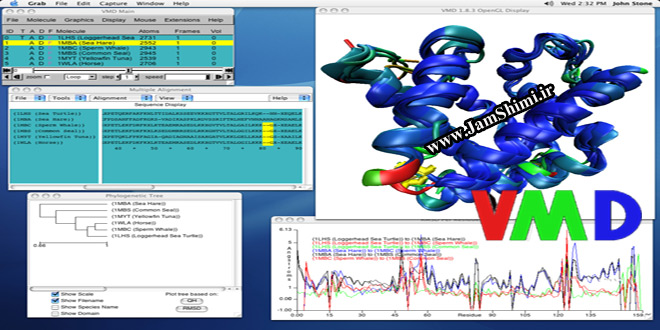
VMD یا Visual Molecular Dynamics یک برنامه کامپیوتری تجسم و مدل سازی مولکولی است. VMD عمدتا ابزاری برای مشاهده و تجزیه و تحلیل نتایج شبیه سازی دینامیک مولکولی است. همچنین شامل ابزارهایی برای کار با دادههای حجمی، دادههای توالی و اشیاء گرافیکی دلخواه است. صحنههای مولکولی را میتوان به ابزارهای رندر خارجی مانندPOV-Ray ، RenderMan ، Tachyon ، Virtual Reality Modeling Language (VRML) و بسیاری دیگر منتقل کرد. کاربران میتوانند اسکریپتهای Tcl و Python خود را در VMD اجرا کنند زیرا شامل مترجمان تعبیه شده Tcl و Python است. VMD بر روی یونیکس، Apple Mac macOS و Microsoft Windows اجرا میشود.
VMD تحت مجوز مخصوص توزیع در دسترس کاربران غیرتجاری است که هم استفاده از برنامه و هم اصلاح کد منبع آن را بدون هیچ گونه هزینهای مجاز میداند. VMD میتواند از طریق Tcl/Tk با برنامههای دیگر ارتباط برقرار کند. این ارتباط امکان توسعه چندین پلاگین خارجی را فراهم میکند که با VMD کار میکند. این افزونهها مجموعهای از ویژگیها و ابزارهای VMD را افزایش میدهد و آن را به یکی از پرکاربردترین نرم افزارها در شیمی محاسباتی، زیست شناسی و بیوشیمی تبدیل میکند.
IGV (12
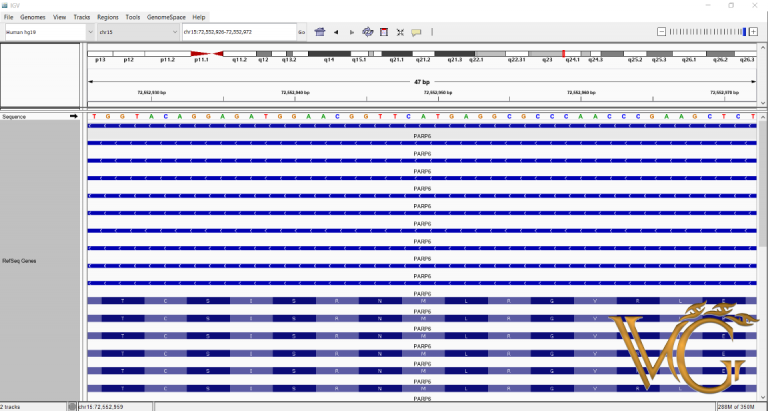
Integrative Genomics Viewer یا IGV یکی از نرم افزارهای بیوانفورماتیک تعاملی با کارایی بالا، استفاده آسان و راحت برای کاوش بصری دادههای ژنومی است. این برنامه از ادغام انعطاف پذیر انواع رایج دادهها و فرادادههای ژنومی، ایجاد شده توسط محقق یا در دسترس عموم، بارگیری شده از منابع محلی یا ابری پشتیبانی میکند. IGV در اشکال مختلفی وجود دارد، از جمله IGV اصلی که یک برنامه دسکتاپ جاوا است، IGV – Web که یک برنامه بر پایه وب بوده و igv.js که یک جزء جاوا اسکریپت است که میتواند در صفحات وب جاسازی شود.
گزارش از شکوفه راشدی